景杰学术 | 报道
硝化除磷污泥 (DPRS) 广泛应用于污水处理的脱氮除磷 (如A2 O工艺) ,但可能会受到污水中重金属的胁迫导致效能下降。目前关于微生物抵抗重金属的机制的知识主要基于纯培养物,且有关微生物群落重金属抗性的研究主要集中在土壤或沉积物上,仍然缺乏对复杂DPRS群落中微生物重金属抗性的了解,阻碍了重金属胁迫下工艺的优化。 近日,南京大学 任洪强 院士 团队在微生物顶刊 Microbiome 上发表了题为“ Revealing taxon-specific heavy metal-resistance mechanisms in denitrifying phosphorus removal sludge using genome-centric metaproteomics ”的研究论文。文中 利用宏蛋白质组学技术揭露了活性污泥中硝化菌和聚磷菌的重金属抗性,展现了复杂污泥体系下微生物重金属抗性的多样异质性。
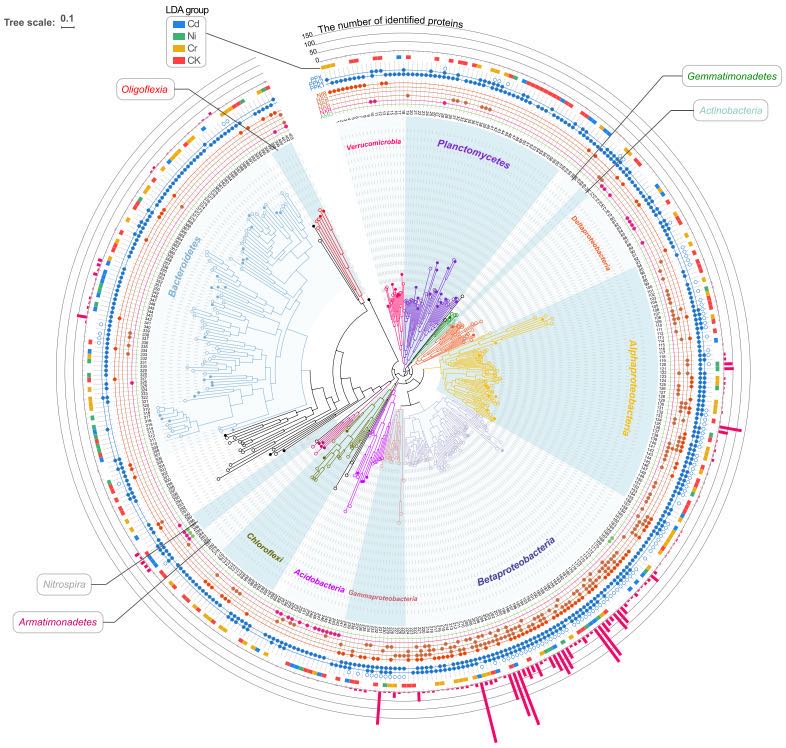
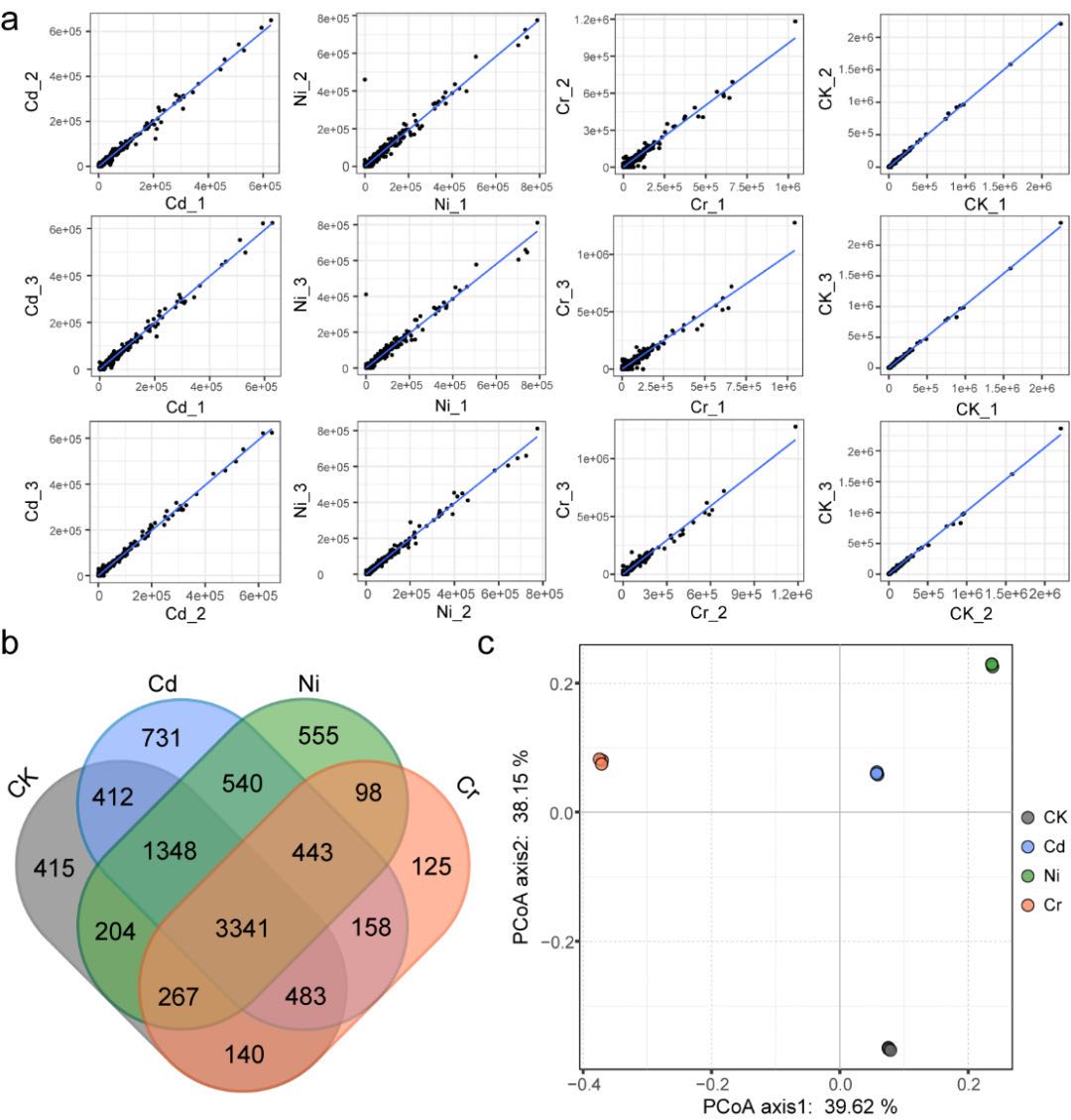
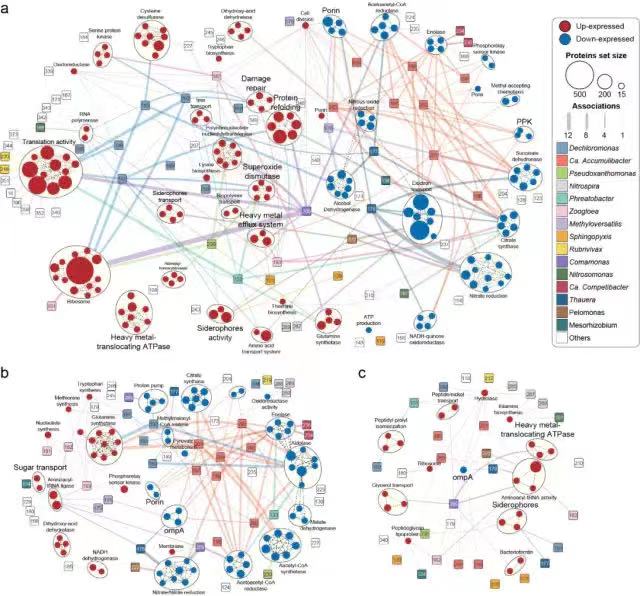
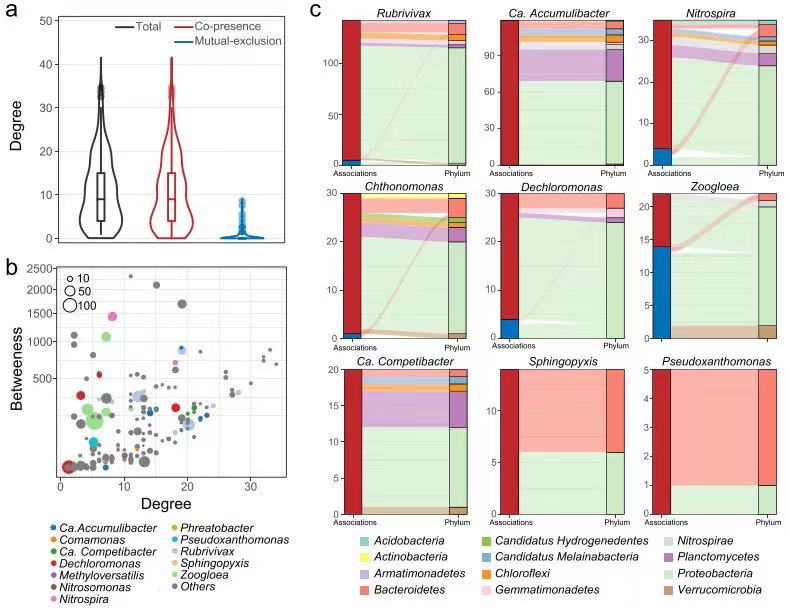
作者从三种不同重金属 (Cd、Ni和六价Cr) 在不同浓度暴露下的DPRS中,聚类分析获取了共403个满足MIMAG严格标准草图基因组 (MAG) 。通过比较MAGs的分类图谱和从亚基因组核糖体蛋白基因rplB预测的分类图谱,确认获取的MAGs是DPRS中优势类群的代表。 对于复杂群落而言,宏蛋白质组学提供了将分类特性与重金属抗性相关的活性表达功能联系起来的机会。基于得到的MAG,研究人员进一步通过Label free蛋白质组学定量技术,研究了不同微生物的蛋白组在重金属暴露下的变化,并重点关注那些与氮磷去除和重金属抵抗相关的功能蛋白。研究共鉴定到9537个蛋白质,其中7973个蛋白具有有效的定量信息。主成分分析表明重金属引起的不同的宏蛋白质组组成,不同反应器中仅有3341 (35%) 种蛋白质重合。 为了更全面地了解重金属抗性机制,研究人员利用富集分析对胁迫条件下的差异表达蛋白进行了表征,并鉴定了有助于这些显著富集功能的核心功能微生物。高浓度重金属胁迫导致氧利用率低下,硝化菌决定了DPRS中的氮去除。完全硝化菌Nitrospira 产生大量的氧亲和血红素蛋白以增强氧气的获取和利用。而氨氧化菌Nitrosomonas 则依赖过表达氨氮加氧酶和亚硝氮还原酶以驱动短程硝化反硝化过程,从而维持重金属胁迫下的氨氮去除。而DPRS中的磷去除由聚磷菌 (PAOs) Candidatus Accumulibacter 和Dechloromonas 决定。两者基因组上显示出极大的相似度,但在重金属抵抗机制上表现出很大的不同。其中最明显的是在重金属暴露下Dechloromonas 比Candidatus Accumulibacter 在多聚磷酸(polyP) 的合成上优势显著。而polyP可以作为一种广泛的重金属解毒物质,保护整个微生物群落。此外,Dechloromonas 还比Candidatus Accumulibacter 在能量利用,自由基消除和损伤细胞修护方面更具优势。 研究发现涉及重金属细胞外解毒的微生物衍生物质不仅对生产者有利,而且对环境中的其他成员也有利,导致一些本不应该抵抗重金属的类群 (如硝基螺) 在环境中也能大量存活。种间关联分析生成了由181个微生物 (节点) 和964个种间联结 (边缘) 组成的MAG间关系网络。其中大多数估计的关联是正的,而只有33种互动是负的,说明在重金属压力下,DPRS微生物组更喜欢合作互动而不是竞争关系。 综上所述,该研究 运用宏基因组学、宏蛋白质组学研究了重金属压力下DPRS微生物组的适应性和抗性特征 。 证实了复杂微生物群落中的不同微生物的重金属抗性是极其多样化的,为后续系统优化提供了理论指导。同时证实了宏蛋白质组学能够有效应用于了解复杂群落中微生物在不利条件下的适应机制。
Yuan Lin, et al. , 2021, Revealing taxon-specific heavy metal-resistance mechanisms in denitrifying phosphorus removal sludge using genome-centric metaproteomics. Microbiome
本文由景杰学术 团队报道,欢迎转发到朋友圈。如有转载、投稿等其他合作需求,请文章下方留言,或添加微信ptm-market咨询。
转载本文请联系原作者获取授权,同时请注明本文来自卜晨科学网博客。 https://wap.sciencenet.cn/blog-3404471-1292647.html
上一篇:
“真”于心,“单”于一 | 真·单细胞蛋白质组学耀世而至 下一篇:
特邀973首席科学家谢鹏教授,聚焦“微生物稳态与重大疾病调控”